教程1:ASA GUI 端到端分析教程¶
本教程介绍 ASA GUI(Attractor Structure Analyzer)如何将 ASA pipeline 的数据预处理、 TDA、解码与可视化整合为图形化工作流。你将学会用窗口界面完成分析并在结果目录中管理输出。
Note
若想深入了解分析原理与参数选择,请参阅 教程1:ASA Pipeline:实验数据解码全流程。
教程目标¶
使用 ASA GUI 完成一次端到端分析
理解输入数据结构、参数含义与输出目录
掌握常见分析模式与依赖关系
适用人群¶
需要图形界面完成 ASA pipeline 的用户
想快速浏览分析结果与图表的实验研究者
希望复用 TDA/解码/可视化流程的实验组
前置准备¶
已安装 CANNs(建议
pip install -e .或pip install canns)安装 GUI 依赖:
pip install canns[gui](包含 PySide6)可选:
pip install qtawesome(用于导航栏图标)准备好 ASA
.npz数据
Note
ASA GUI 当前仅支持 ASA .npz 输入。 “Neuron + Trajectory” 相关控件仍处于预留状态。
启动 ASA GUI¶
在项目环境中执行:
canns-gui
# 或
python -m canns.pipeline.asa_gui
启动后会显示主窗口,默认尺寸约 1200×800,可根据屏幕调整大小。
界面概览¶
主窗口顶部包含:
Preprocess 与 Analysis 导航按钮
Light / Dark 主题切换
Help 帮助按钮(打开快速使用说明)
中文 / English 双语切换
Preprocess 页:输入配置、预处理参数与日志。 Analysis 页:分析参数、结果预览与文件输出。
界面元素清单¶
Preprocess 页面¶
Input / Mode |
固定为 |
Preset |
预设模板: |
ASA file |
拖拽或点击 Browse 选择 |
Preprocess / Method |
选择 |
Embedding 参数 |
|
Pre-classification |
预留选项( |
Run / Stop / Progress |
启动或终止预处理,并显示进度条。 |
Logs |
显示预处理过程日志。 |
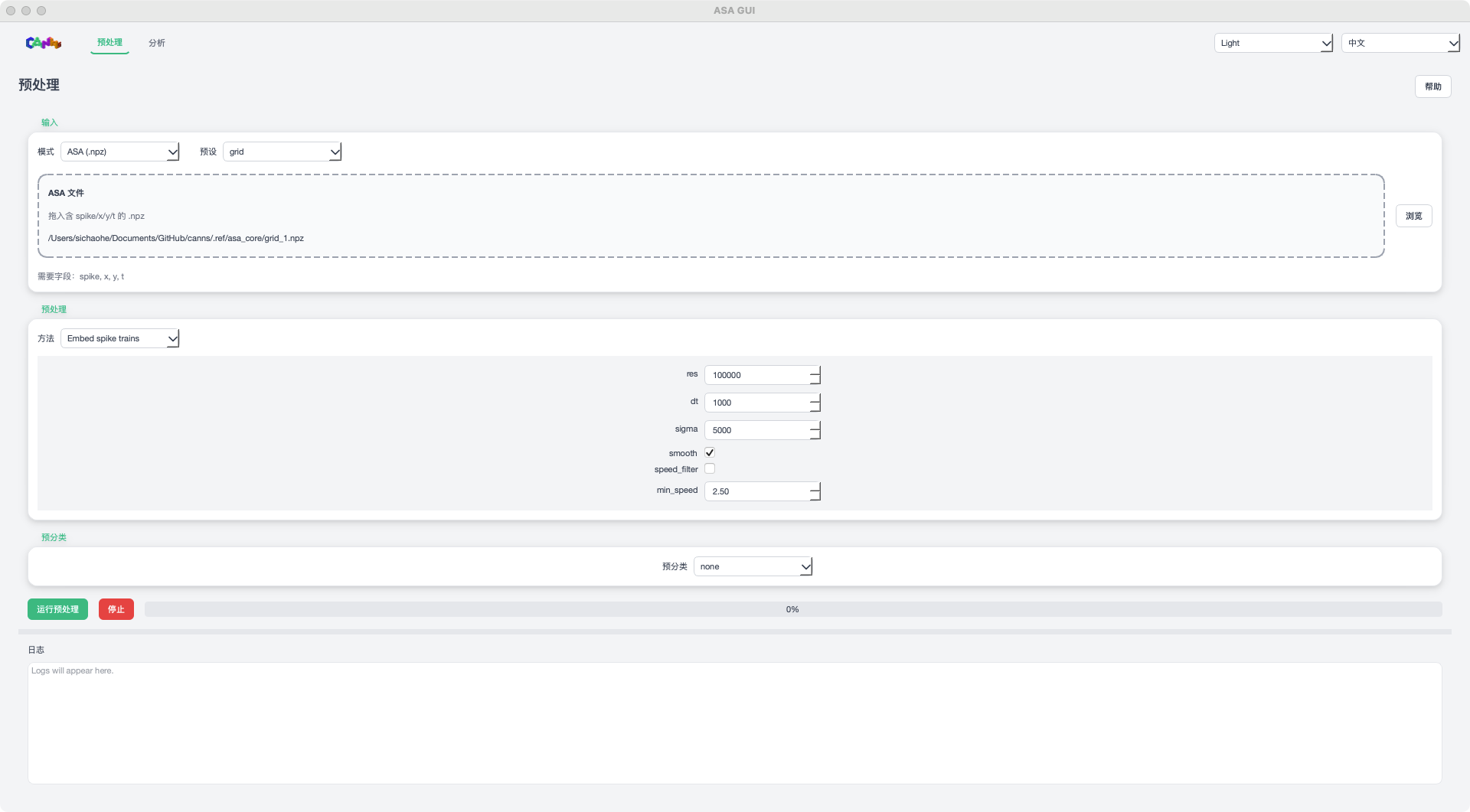
ASA GUI 预处理页(占位图)¶
Analysis 页面¶
Analysis Parameters |
选择分析模块并设置参数。 |
Analysis module |
支持 |
Preprocess (Standardization) |
|
Help |
打开快速帮助与常见提示。 |
Language |
在中文 / English 之间切换界面语言。 |
Run Analysis / Stop / Progress |
运行分析并显示进度。 |
结果标签页 |
|
Files |
列出输出文件并可 Open Folder 打开结果目录。 |
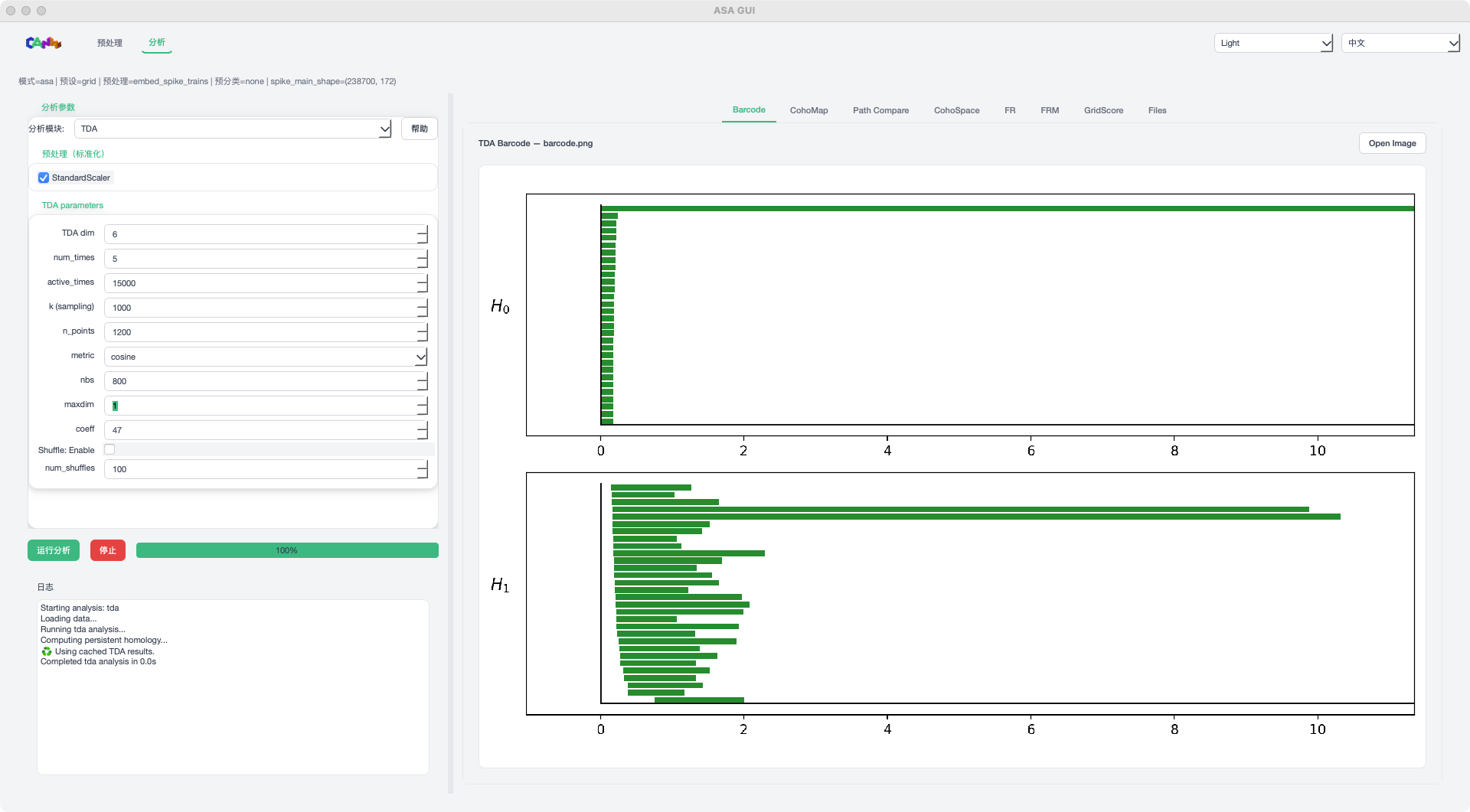
TDA 模式示例¶
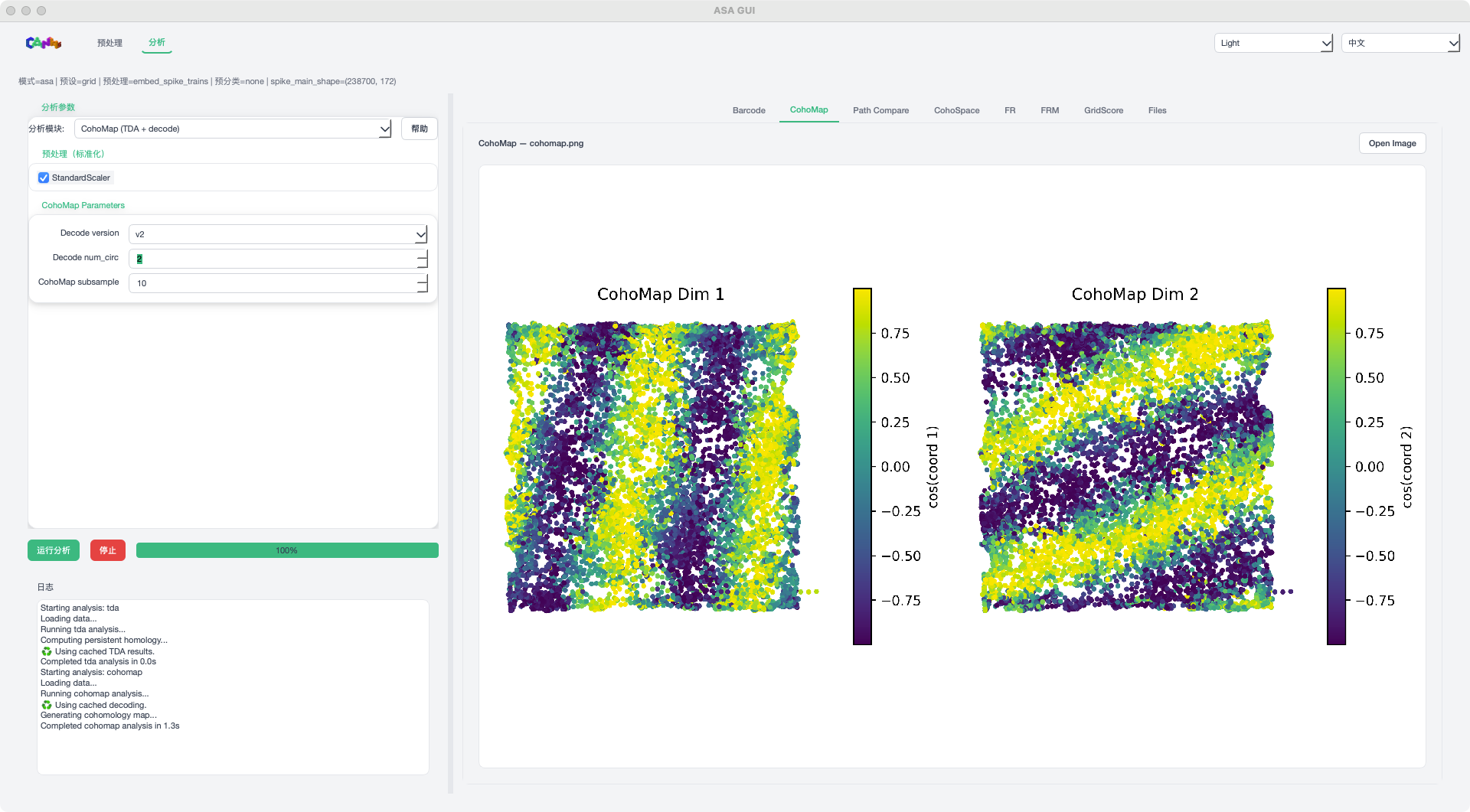
CohoMap 模式示例¶
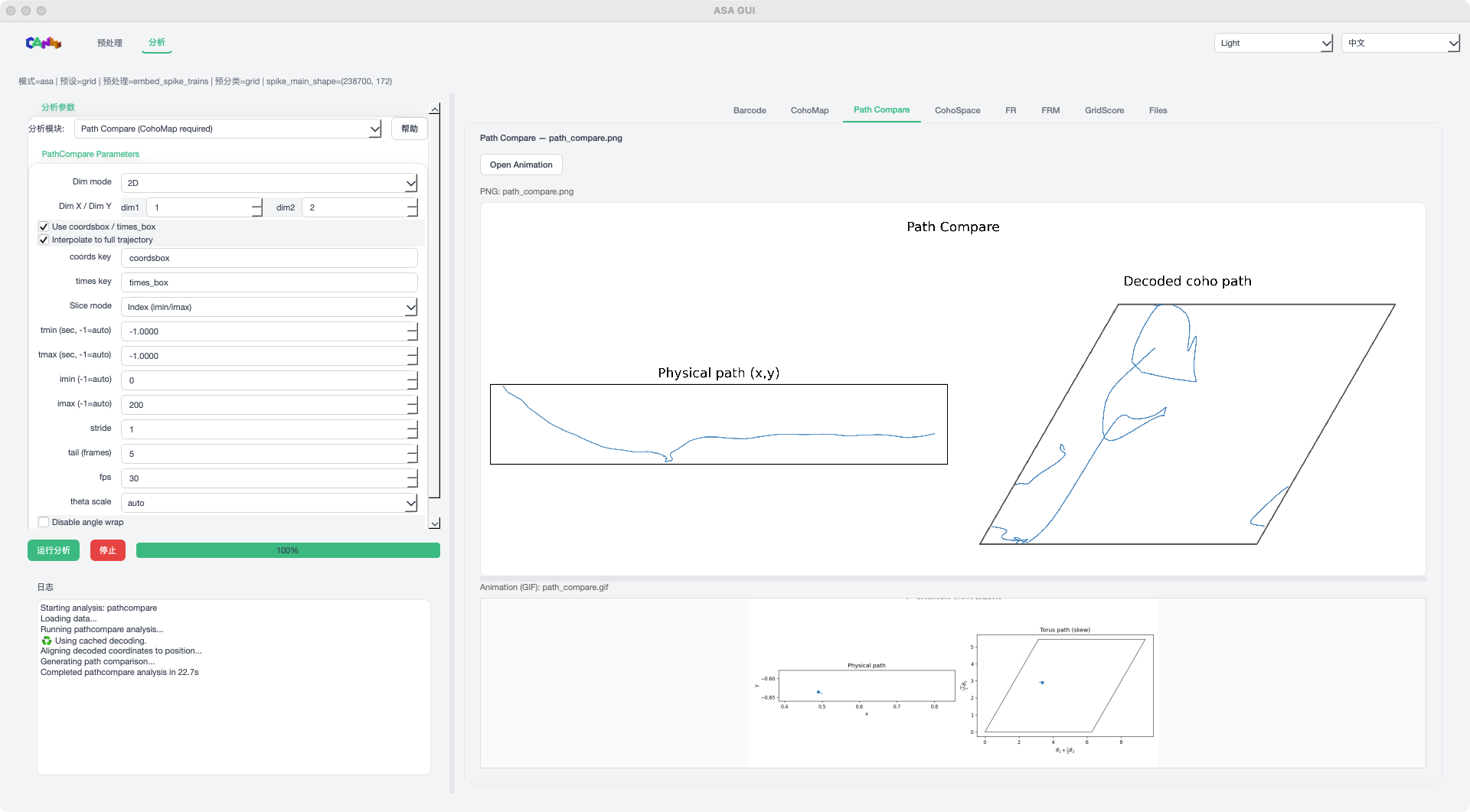
Path Compare 模式示例¶
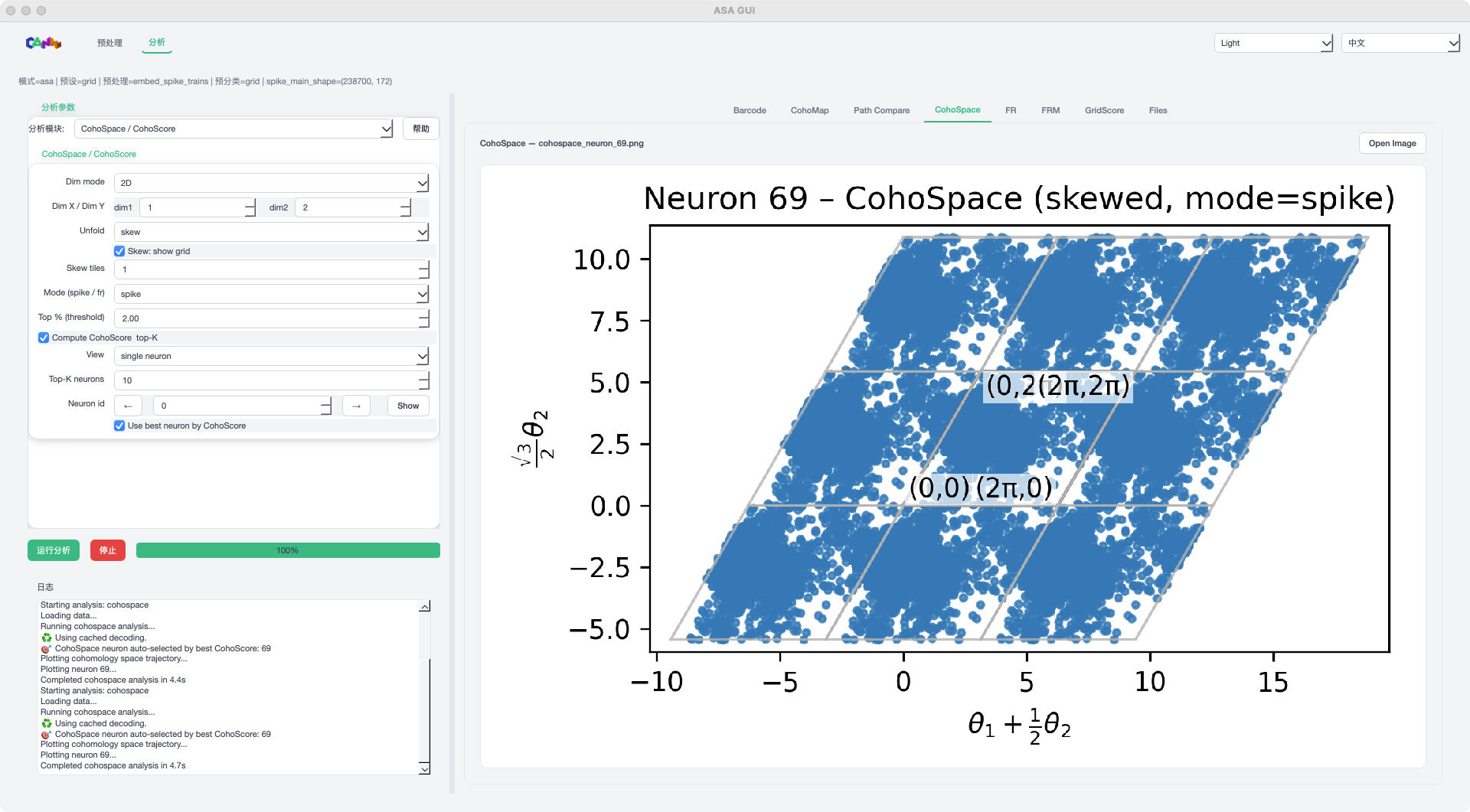
CohoSpace 模式示例¶
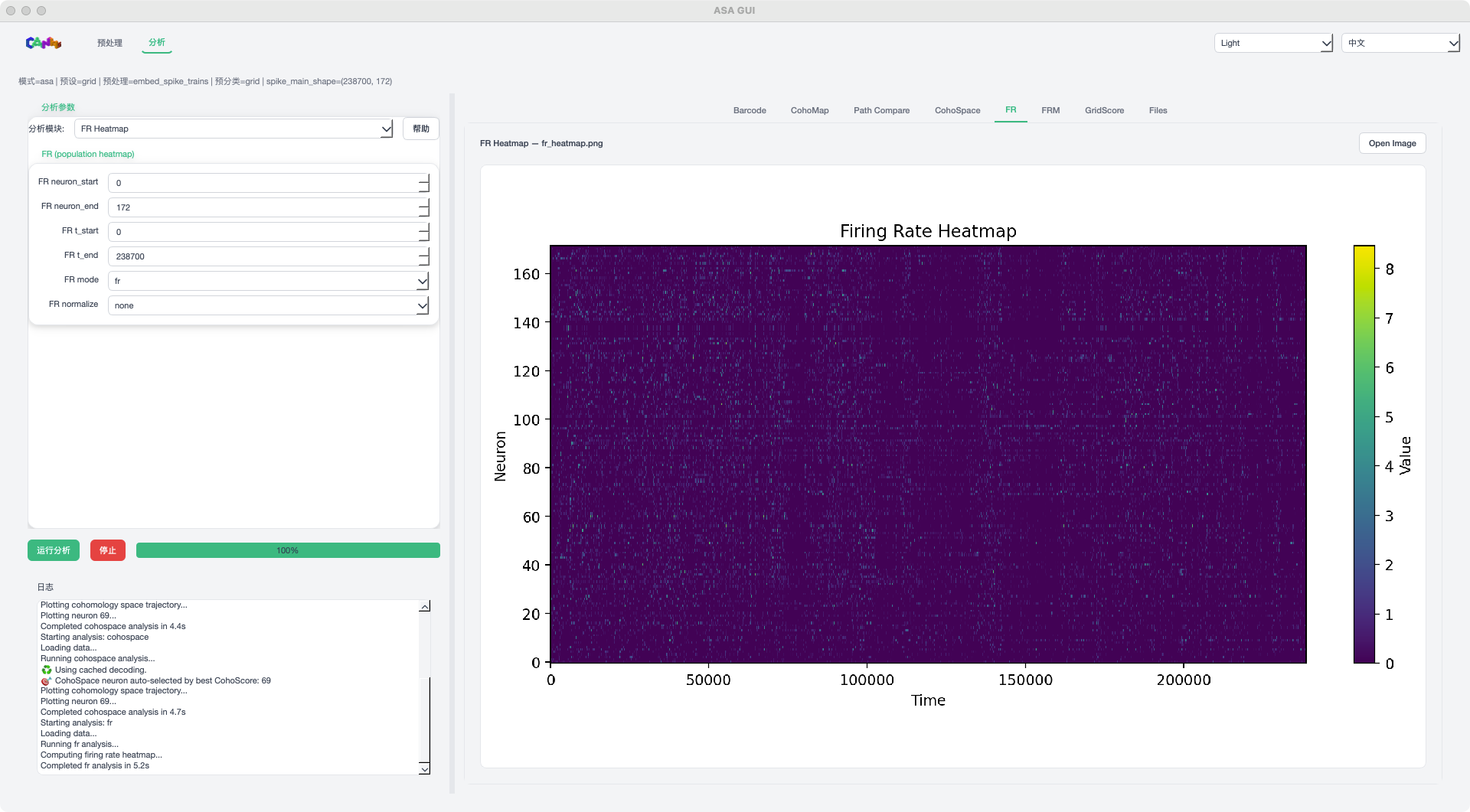
FR 模式示例¶
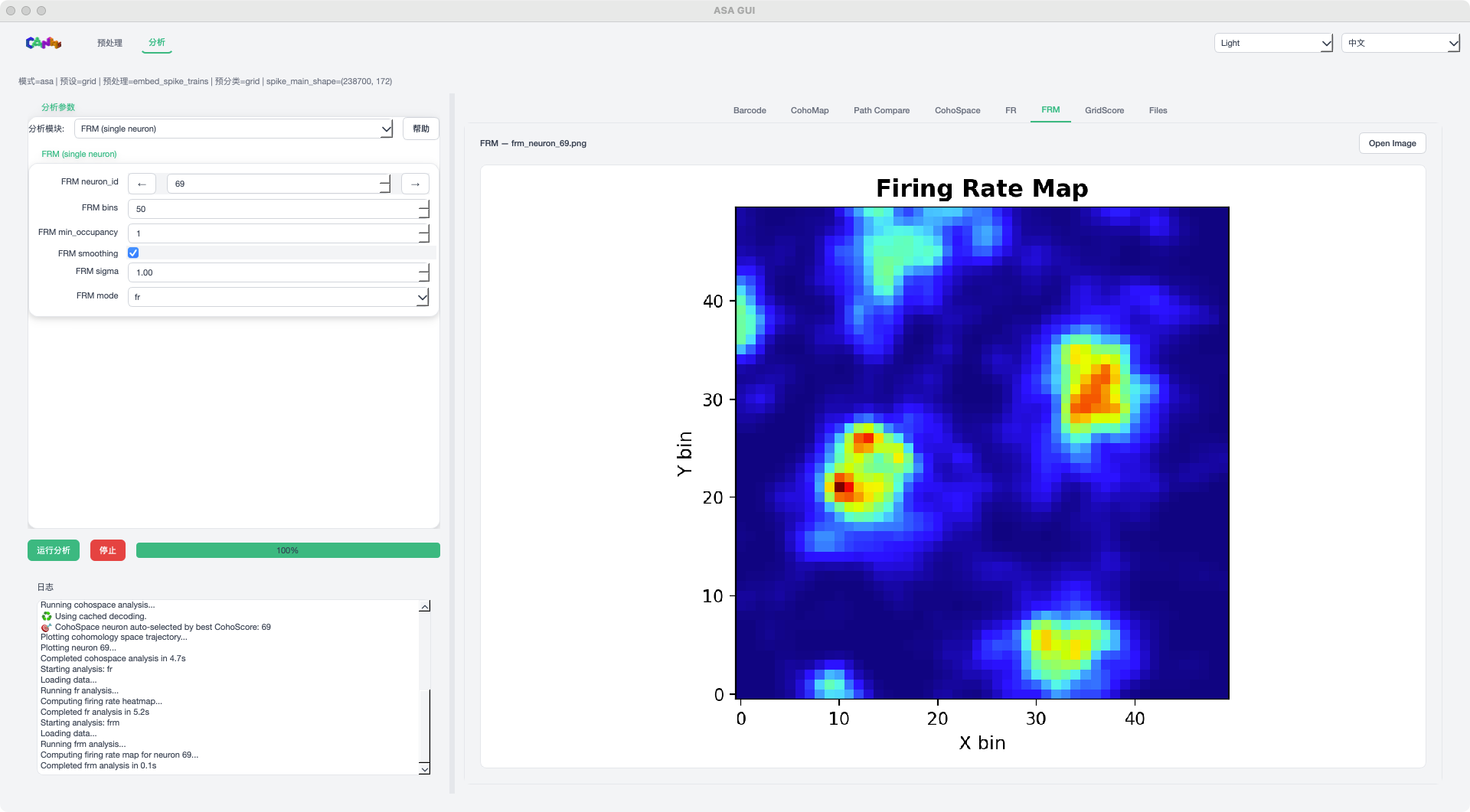
FRM 模式示例¶
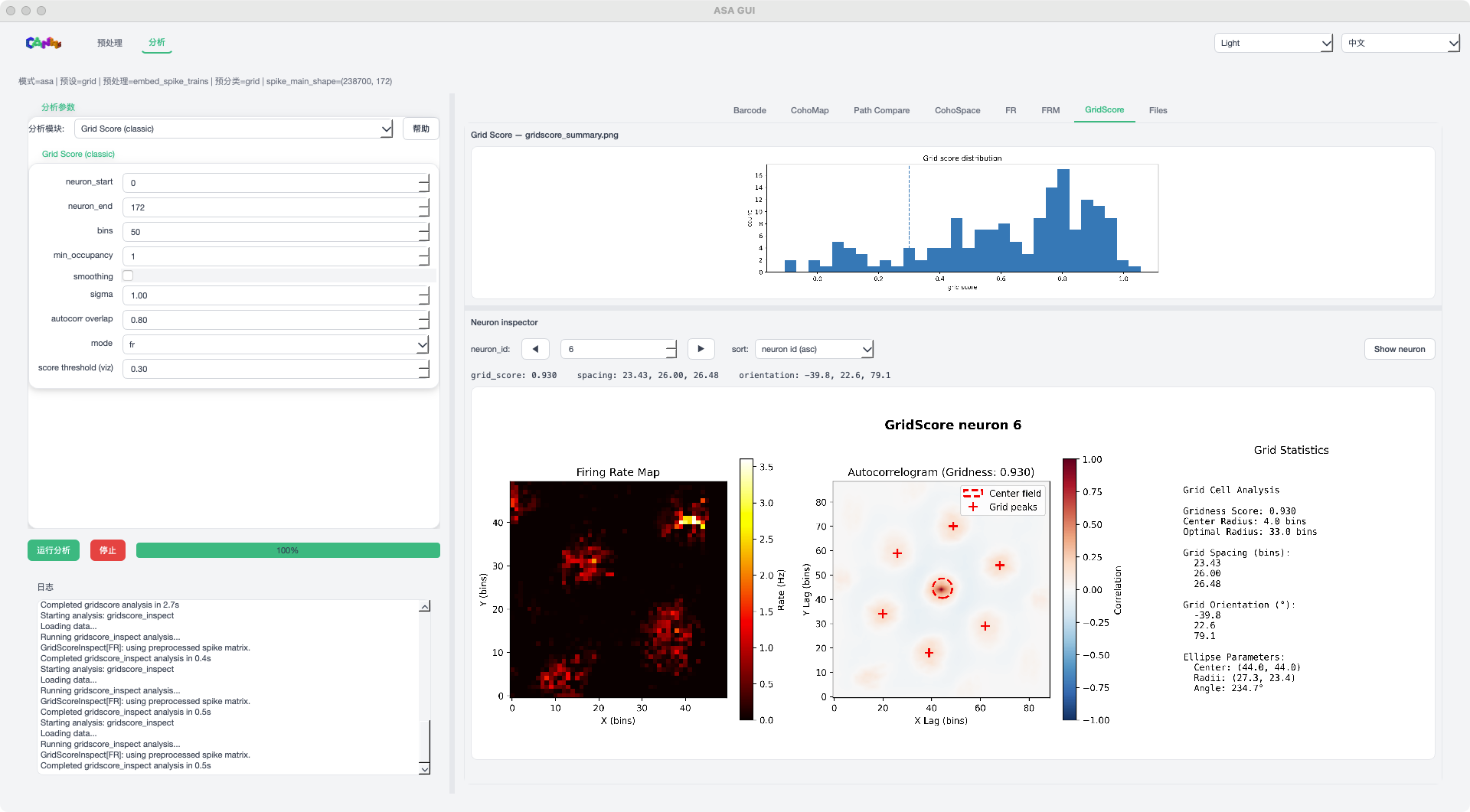
GridScore 模式示例¶
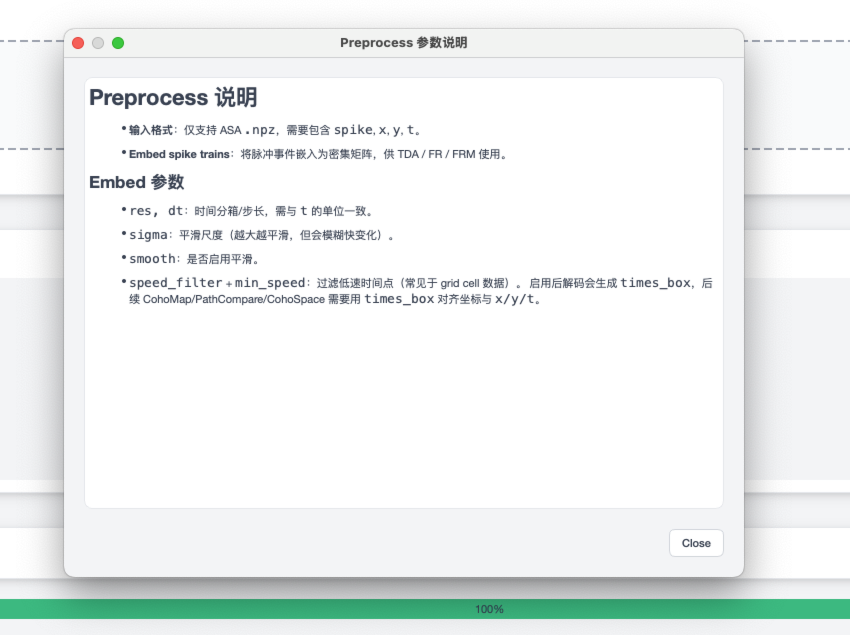
Preprocess 帮助面板¶
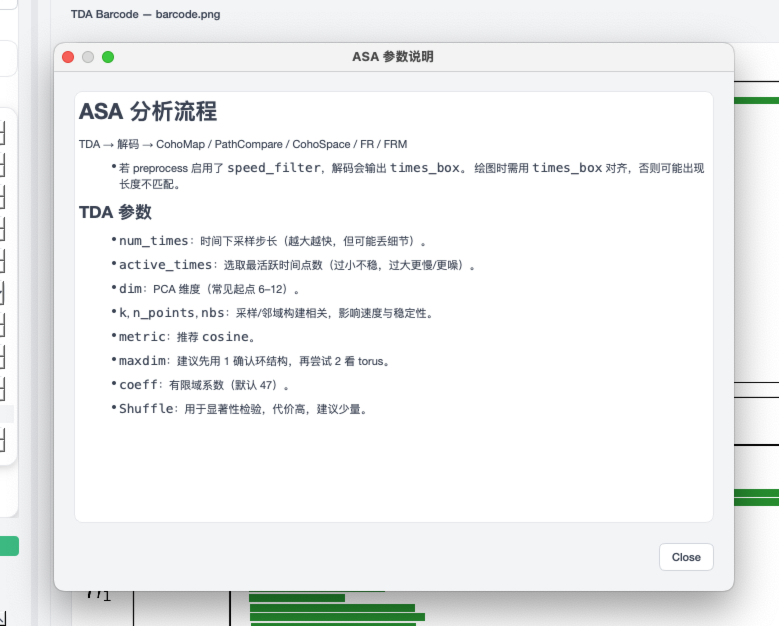
TDA 帮助面板¶
工作流程概览¶
启动 ASA GUI
选择 ASA
.npz输入文件配置预处理参数并运行 Preprocess
进入 Analysis 页选择分析模块
运行分析并在标签页查看结果
步骤 1:选择 ASA 文件¶
在 ASA file 区域拖拽或点击 Browse 选择 .npz 文件。
界面会提示期望的字段:spike / x / y / t。
ASA 文件格式¶
至少包含 spike 与 t:
spike:T x N的稠密矩阵,或可嵌入的 spike 数据结构t: 时间序列(与spike同步)可选:
x/y用于轨迹相关分析
import numpy as np
np.savez(
"session_asa.npz",
spike=spike,
t=t,
x=x,
y=y,
)
步骤 2:设置预处理¶
在 Preprocess 区域选择预处理方法:
None:直接使用原始 spike 结构
Embed spike trains:生成稠密矩阵供 TDA/FR/FRM 使用
如需嵌入,设置 res / dt / sigma / smooth /
speed_filter / min_speed 等参数,然后点击 Run Preprocess。
步骤 3:选择分析模块¶
切换到 Analysis 页面,选择分析模块并配置参数:
TDA:持久同调分析与条形码
CohoMap / CohoSpace:解码并绘制空间结构
Path Compare:轨迹比较(含动画输出)
FR / FRM:放电率热图与神经元放电率图
GridScore:网格评分与神经元浏览器
点击 Run Analysis 开始运行。
步骤 4:查看结果¶
运行完成后,在右侧标签页查看结果:
图像标签页:支持内嵌预览与 Open Image 外部打开
GridScore:包含分布图与神经元 inspector
Files:列出输出文件并可打开输出目录
结果输出结构¶
输出目录默认位于当前工作目录下:
Results/<dataset>_<hash>/
其中 <dataset> 由输入文件名生成,<hash> 为输入哈希前缀。
目录中会包含分析结果与缓存(.asa_cache),以加速重复运行。
注意事项¶
GUI 的工作目录为 启动 GUI 时的当前目录,可在命令行中切换目录后再启动。
如果需要
Neuron + Trajectory输入,请使用 ASA TUI 或脚本流程。